比利时VIB-KU Leuven的Stein Aerts教授团队近期在《自然方法》期刊上发表了一项新研究,提出了一种名为CREsted的软件包,旨在以系统化和可扩展的方式分析和设计基因调控元件。这一工具解决了人工智能在解码DNA调控逻辑时面临的应用难题,特别是针对不同数据集、组织和物种的挑战。
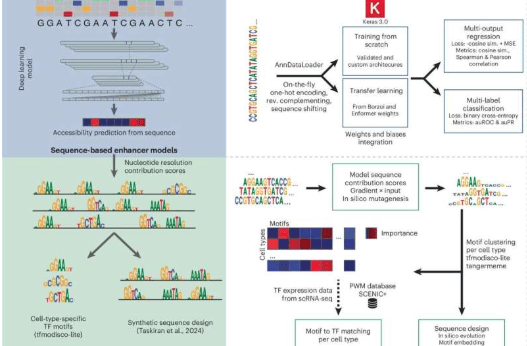
基因调控元件如增强子,是控制基因活性的短DNA序列,但现有方法往往局限于单一数据集,难以重用或扩展。CREsted框架将增强子建模从一次性分析转变为更系统化的工作流程,整合了预处理、模型训练、解释和合成增强子设计等步骤,并适配单细胞分析流程,便于研究人员采用。
“我们希望超越一次性模型,”Aerts实验室的博士生Niklas Kempynck说。“CREsted允许研究人员系统研究生物系统中的增强子逻辑,从可访问调控DNA的逐个细胞图谱开始,一直到序列设计。”与Kempynck共同第一作者的Seppe De Winter博士补充道:“通过CREsted,我们为研究人员提供了一个完整的工作流程。你可以在染色质可及性数据上训练深度学习模型,解释它们捕获的调控特征,然后使用这些模型设计具有预测细胞类型特异活性的新DNA序列。”
该团队已将CREsted应用于小鼠脑组织、人类免疫细胞、癌细胞状态和斑马鱼发育等多个系统,成功识别调控模式、预测增强子活性,并设计出在斑马鱼体内验证的合成增强子。VIB.AI的科学主任Stein Aerts教授表示:“CREsted使训练、解释和比较不同数据集的增强子模型变得更加容易。如果我们希望这些方法变得广泛有用,这不仅对于理解调控DNA,而且对于以系统方式设计和测试新序列,这一点很重要。”
这项研究展示了人工智能如何推动基因调控领域从描述转向探索和设计,为基因调控元件的研究提供了更系统化的工具,在基础生物学、生物技术和医学领域具有应用潜力。
出版详情:作者:VIB (the Flanders Institute for Biotechnology);标题:《Software package makes gene regulation easier to study—and tweak》;发表于:《Nature Methods》(2026);期刊信息: Nature Methods
